《食品科学》:中国农业大学赵卿宇副教授等:近红外光谱技术在谷物检测中的应用研究进展
- 2026-05-24 23:37:15
谷物是指一类主要用于食用的禾本科植物的籽粒,包括小麦、水稻、玉米等。谷物在储存、运输、销售过程中随着时间和环境的改变,其主要成分往往会发生变化,这些会导致谷物口感和品质变差,更严重的可能会引发霉变,进而产生霉菌毒素等有毒物质。
近红外光谱技术是一种常见的快速无损检测技术,其原理主要基于分子振动和旋转能级的跃迁,当近红外光谱照射到样品上时,样品中的含氢基团会吸收特定波长的光能,引起分子内部键的倍频、合频振动和旋转跃迁。不同的分子结构和化学键对近红外光的吸收特征不同,形成特定的光谱图。该技术已被广泛应用于水产品新鲜度检测,谷物、油料理化指标的检测,以及谷物、乳制品营养成分分析等。
中国农业大学食品科学与营养工程学院的王子熙、沈群、赵卿宇*主要对近红外光谱技术在谷物中营养成分、理化性质、霉菌污染以及其他方面的应用进行介绍,总结比较常用的算法,并展望近红外光谱技术在谷物检测方面的发展前景(图1)。
1 近红外光谱技术在谷物营养成分分析中的应用

谷物中的淀粉、蛋白质、脂肪等成分含氢基团丰富,在近红外光照射下不同含氢基团会发生合频和倍频吸收,形成特定的吸收光谱,基于化学计量学方法,通过不同的计算方法建立模型,可以检测未知样品的组分含量。Xie Lihong等采集了129 个水稻的近红外光谱,结合修正偏最小二乘法(MPLS)建立了水稻表观直链淀粉、直链淀粉和支链淀粉的模型,模型校正决定系数分别为0.977、0.928、0.912。张北举等采集了112 份高粱品种,扫描了850~1 048 nm的近红外光谱,采用多种光谱预处理并结合改进偏最小二乘(PLS)法建立高粱中直链淀粉、支链淀粉含量的预测模型,结果表明,采用标准正态变换(SNV)和二阶导数处理后的模型能够最精准地预测高粱的直链淀粉含量,相关系数为0.968 8;采用SNV和一阶导数处理后的模型能够最精准地预测高粱支链淀粉的含量,相关系数为0.912 7。脂肪在谷物中的含量相对较低,但对谷物的风味影响较大。陈素彬等采集了76 份玉米籽粒的近红外光全光谱,结合最小二乘支持向量机(LSSVM)法建立玉米脂肪含量的定量模型,并通过量子行为粒子群优化法结合留一法交叉验证对模型参数进行优化,提高了模型的精准度和稳定性,与传统的PLS校正模型相比,该方法建立的模型相关系数有所提高,从0.961 8提升到0.993 4。Lin Chen等通过近红外光谱技术结合最小二乘支持向量回归(LSSVR)、PLS和径向基函数神经网络3 种多元校正方法基于227 个大麦样本建立了大麦籽粒蛋白质含量的模型,结果表明,LSSVR模型的相关系数高于其他两种模型,为0.983 6,预测效果更精准。Wu Xiaohong等采集了玉米的近红外光谱,通过锚点竞争性自适应重加权采样法对特征波长进行选择,并结合PLS建立玉米蛋白质含量的定量模型,模型的校正决定系数为0.995 1,预测决定系数为0.982。刘文丽等采集了大米的近红外光谱,结合PLS建立大米蛋白质和蛋白质干基的近红外模型,两种模型内外部校正决定系数均大于0.95。从以上研究可以看出,近红外光谱技术检测谷物淀粉含量时适合采用修正PLS模型,检测大米和玉米蛋白质含量时适合采用PLS建立模型,而检测大麦蛋白质和玉米脂肪含量时采用LSSVM模型比PLS模型更精准。因此,对于单一营养物质的检测,针对不同谷物品种不同物质建立的最适模型不同。
然而多数情况下,需要采用一种模型同时分析出谷物的多种营养成分,因此要找到一个折中的算法。沈广辉等采集了171 份玉米籽粒的近红外光谱,通过竞争性自适应重加权采样法筛选变量,并结合PLS建立玉米籽粒水分、粗蛋白、粗灰分和总能量的定量模型,模型的校正决定系数依次为0.90、0.92、0.78、0.92,预测决定系数依次为0.76、0.89、0.72、0.83。王蓉等通过主成分分析对光谱进行筛选并建立了80 份不同玉米中水分、脂肪、蛋白质、淀粉的一维卷积神经网络(1DCNN)模型,并将其与传统近红外光谱PLS或支持向量机模型进行对比,结果表明,1DCNN模型的决定系数分别为0.990 9、0.981 5、0.988 9、0.996 0,比传统方法更接近于1。因此,采用主成分分析光谱法结合1DCNN建立的模型比竞争性自适应重加权采样法结合PLS建立的模型更能准确检测玉米的多种营养成分。Bagchi等采集了173 份糙米的近红外光谱,通过SNV和导数处理对光谱进行预处理,并结合MPLS建立糙米直链淀粉、籽粒蛋白质和米糠水分、灰分等近似成分的校正模型,其中直链淀粉和蛋白质的决定系数分别为0.918和0.859,米糠近似成分的相关系数为0.720~0.964。黄林森等采集了75 份大米的近红外光谱,结合多种光谱预处理和3 种建模方法建立大米主要营养成分的定量模型,结果表明,对于大米中碳水化合物和蛋白质通过一阶导数与Savitzky-Golay(SG)卷积平滑法对光谱预处理,对于水分和脂肪通过二阶导数与SG对光谱预处理,二者结合PLS建立的定量模型具有高精准度,相关系数分别为0.917 5、0.919 8、0.933 3、0.926 6。由此可见,对于大米营养物质的检测,采用PLS建立的模型得到的精准度比修正PLS模型更高。陈静采集了小米的近红外光谱,通过3 种波长筛选法结合两种建模方法建立小米碳水化合物、脂肪、蛋白质和多种氨基酸等营养成分的预测模型,研究发现,对于小米的蛋白质和不同氨基酸,与全光谱、JK算法结合的PLS模型和间隔PLS模型相比,连续投影算法(SPA)结合多元线性回归(MLR)模型使用的波长较少且准确性更高。综上,玉米的多种营养成分指标检测更适合采用1DCNN模型,大米的多种营养成分检测采用PLS更有效,而小米的蛋白质和多种氨基酸检测更适合采用MLR模型。
除谷物中的宏量组分外,近红外光谱技术还可以对多种微量生物活性物质,如非淀粉多糖、酚类化合物等进行精准检测。Albanell等通过近红外光谱技术结合光谱预处理和MPLS建立了186 份大麦的生物活性物质含量的预测模型,结果表明,模型对β-葡聚糖和结合酚的预测效果较好,决定系数分别为0.967和0.898,但对花青素、阿拉伯聚糖的预测效果较差。Yang Zhongyu等采集了63 份燕麦籽粒的近红外光谱,通过平方预处理建立燕麦β-葡聚糖的SPA-MLR模型,模型验证相关系数为0.84,均方根误差为0.55,预测效果良好。Johnson等采集了65 份小麦的近红外光谱,通过一阶导数和标准正态变化法对光谱预处理,建立小麦总酚含量和总单体花青素的PLS模型,结果表明,该方法对小麦总酚含量的预测准确率较高,决定系数为0.83,但对花青素预测效果不理想。由此可知,对于大麦中β-葡聚糖和结合酚及小麦中总酚含量采用PLS模型分析能够得到较精准的结果,而对燕麦中的β-葡聚糖适合采用MLR模型进行分析。值得注意的是,以上研究对于花青素的预测效果均不理想,原因可能在于花青素在这些谷物中含量较低或数据集的最小值和最大值之间的时间间隔较窄,导致近红外光谱技术无法精准检测。
此外,需要注意的是,近红外光谱技术建立的修正PLS模型仅适合检测大麦β-葡聚糖和结合酚的含量,但对于大麦的其他营养成分检测不够灵敏,或者无法准确检测。从现有的文献看,近红外光谱技术并不能用于谷物中所有微量生物活性物质的分析,需要进一步探索更优算法且需要大量的样品数据对建立的模型进行校正和验证以获得更准确的结果。以上研究结果和总结见表1。
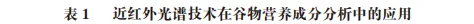
 |  |

2 近红外光谱技术在谷物理化性质中的应用

谷物的理化性质指标包括千粒质量、硬度、淀粉黏度特性值以及粉质特征等指标,尽管这些理化指标不属于谷物的组成成分,但与谷物中营养成分的组成密切相关,能反映营养物质的组成特性。因此,通过分析与谷物理化性质相关的营养成分的近红外光谱,结合不同化学计量法建模,可以实现对谷物理化指标的检测。
崩解值和消减值与谷物的淀粉含量相关,反映了大米淀粉的黏滞特性,Burestan等通过近红外光谱技术采集了109 份(校准集81 份、验证集28 份)大米870~2 450 nm的近红外光谱,并结合PLS建立白米理化指标崩解值和消减值的校正模型。结果表明,校正决定系数分别为0.984和0.927,预测决定系数分别为0.954和0.793,校正集的RMSEC分别为2.59和3.11。胶稠度和碱消值由大米直链淀粉含量和热力学变化决定,Cheng Weimin等通过近红外光谱技术分别建立了537 份和527 份大米胶稠度和碱消值的PLS模型,通过最大最小标准化处理的模型对大米胶稠度预测值最好,决定系数为0.921 3,通过MSC处理的模型对大米碱消值的预测效果最好,决定系数为0.872。谷物千粒质量和硬度与谷物碳水化合物和蛋白质密切相关,千粒质量减小,谷物碳水化合物中C—H键发生伸缩和弯曲,可导致近红外光谱的显著变化。小麦硬度主要与所含的Friabilin蛋白含量有关,因此,近红外光谱技术通过检测N—H基团的特定光谱可以实现对小麦硬度的检测。Mishra等使用傅里叶变换近红外光谱技术结合PLS建立了128 份小麦千粒质量和硬度的近红外模型,结果表明,模型的决定系数分别为0.907和0.912,交叉验证值的均方根误差分别为0.576和0.762。王佳楠通过近红外光谱技术扫描了109 份小麦,结合SPA提取特征光谱并建立小麦硬度值的径向基函数神经网络模型,相关系数为0.92。研究发现,近红外光谱技术还可以分析小麦的粉质参数、拉伸参数等理化指标。淀粉与水分子结合后,淀粉分子之间以及淀粉与水分子之间H—O和C—H基团发生复杂的伸缩振动,使得近红外光谱产生特定的吸收峰,可以实现对谷物粉质和拉伸特性的检测。Chen Jia等采集了96 份小麦粉样品的近红外光谱,结合多种光谱预处理建立小麦粉质参数的PLS模型,模型的相关系数均低于0.8,预测效果并不理想。Cui Chenhao等采集了1 028 份小麦粉样品的近红外光谱,结合高斯过程回归和PLS建立吸水率、面团形成时间、面团稳定时间、面团弱化度的预测模型,模型的校正决定系数分别为0.904、0.772、0.827、0.818,相比于传统的PLS模型,该建模显著提高了小麦粉质参数的预测性能。因此,高斯回归处理光谱数据可以有效提升近红外光谱技术对小麦粉质参数的预测准确性。Nagel-Held等采集了450 份小麦样品研磨后小麦粉的近红外光谱,结合不同光谱预处理和多种回归方法建立拉伸度、拉伸阻力和拉伸比率的近红外模型,结果表明,模型的决定系数均低于0.5,预测效果不理想。由此可见,近红外光谱技术可以对小麦的粉质参数进行分析,但无法准确检测小麦的拉伸参数。综上,近红外光谱技术检测稻米和小麦的淀粉黏度特征值、千粒质量和硬度时适合采用PLS模型,对于小麦粉质参数的检测模型精确度仍需进一步提高,对于拉伸参数的预测效果并不理想。
近红外光谱技术结合化学计量学方法可以检测谷物的千粒质量、硬度以及粉质参数等理化指标,实现谷物品质的快速分析。但由于近红外光谱技术检测的精准度依赖于所建模型的质量。因此,下一步研究需要结合新型化学计量学方法建立精确度更高、适用性更强的模型,并通过大量样本数据进行验证。
3 近红外光谱技术在谷物霉菌污染分析的应用

谷物在储存、运输或加工过程中可能会受到霉菌(如黄曲霉、青霉、镰刀霉菌等)的侵染,导致谷物质量下降甚至产生对人体有害的霉菌毒素,如玉米赤霉烯酮、恩镰孢菌素、赭曲霉毒素等,这些毒素在近红外波段具有特征性的吸收光谱,但往往含量较低,不易直接检测。近红外光谱技术可以检测谷物受霉菌污染后其化学和光学特性的变化,它与霉菌含量间接相关,可结合化学计量学法建立对霉菌污染的定量和定性分析模型。Ning Hongwei等采集了100 份人为污染霉菌的小麦样品的近红外光谱,对光谱进行平滑处理和散射校正,再进行归一化处理,采用最小绝对值选择和收缩算子算法提取光谱的特征变量,建立了小麦籽粒中玉米赤霉烯酮含量的支持向量机模型,预测相关系数为0.99。恩镰孢菌素是由谷物中镰刀霉菌产生的次生代谢产物,Dos Santos Caramês等采用最小二乘判别分析法对60 份污染或未污染恩镰孢菌素的大麦近红外光谱进行分析并建立判别模型,结果表明,光谱的差异归因于C—H基团和O—H基团的拉伸和弯曲,主要与淀粉、脂肪和蛋白质等营养成分的变化有关,且模型的鉴别灵敏度为100%,鉴别效果良好。Tao Feifei等采集了180 个玉米籽粒的近红外光谱,采用竞争性自适应重加权算法选择与C—C、C—H、O—H相关的特征光谱,建立了两种黄曲霉感染的玉米和健康玉米的PLS判别分析模型,判别准确率为97.78%,表明近红外光谱技术鉴别玉米中黄曲霉的污染是可行的。de Girolamo等采集了229 份受到赭曲霉毒素A污染的小麦样品的近红外光谱,采用PLS判别分析和主成分线性判别分析模型区分低污染和高污染的小麦样品,临界值为2 μg/kg,判别准确率均为94%。综上,小麦霉菌污染的定量分析适合采用支持向量机模型,而谷物霉菌污染的判别分析适合采用PLS判别分析模型。
近红外光谱技术可以通过光谱的吸收强度和特征波段的变化定性检测谷物是否受到霉菌污染,还可以定量推断霉菌污染的浓度。但谷物霉菌污染处于早期阶段或污染程度较低时,相比于传统检测技术,近红外光谱技术对霉菌及其代谢产物的检测灵敏度和精准度相对较低。
4 近红外光谱技术在谷物检测其他方面的应用

近红外光谱技术在谷物其他检测方面也有应用。脂肪酸含量是评判谷物新陈度的一个重要指标,通过测定谷物中游离脂肪酸的C—H化学键(—CH3、H—C=C—H等)在近红外区域的振动响应可以实现对谷物新鲜度的判定。Liu Yachao等采集了96 份储存8 个月的抛光大米的近红外光谱,采用竞争性自适应重加权采样法选择关键变量,并结合PLS建立大米中游离脂肪酸含量的预测模型,校准集和预测集的相关系数分别为0.99和0.98,预测效果良好。Chen Run采集了180 份储存0~6 个月的小麦样品的近红外光谱,采用竞争性自适应重加权采样法和非优势分选遗传算法-III对光谱进行选择,并结合支持向量机法建立小麦游离脂肪酸含量的模型,校正相关系数为0.996 3,均方根误差为0.759 0,预测相关系数为0.989 7,均方根误差为1.251 8。因此,采用支持向量机模型和PLS模型均能够准确检测谷物游离脂肪酸的含量,且采用竞争性自适应重加权采样法对特征光谱进行选择更能提高模型精准度。
虽然近红外光谱技术不能直接检测谷物储存过程中产生的气态化合物,但是通过比色传感器阵列结合近红外光谱技术却可以有效检测谷物的挥发性物质,从而判定谷物的新陈度。Lin Hao等收集了150 份储存了0、1、2、4、6 个月的水稻样品产生的挥发性化合物(如18-冠醚-6、乙醛、丙酮等),使其与比色传感器中氟硼二吡咯染料发生反应,随后使用近红外光谱技术采集反应后染料的光谱数据,通过协同区间PLS对光谱进行处理,并采用线性判别分析法建立了水稻储存月份的鉴别模型,模型校正集和预测集的识别率分别为98.75%和97.5%。预测准确率较高。Liang Yue等同样采用近红外光谱技术结合比色传感器阵列对新鲜和储存2 a的水稻和大豆新陈度进行鉴别,结果表明,遗传算法结合线性判别分析法建立的近红外模型能正确区分100%水稻样品和95.83%大豆样品的新鲜度。由此可见,近红外光谱技术通过检测挥发性化合物对谷物新陈度鉴别时适合采用线性判别分析模型。
近红外光谱技术还可以根据谷物和异种粮粒中营养成分组成(如淀粉、脂肪、蛋白质等)的差异对谷物中异种粮粒以及谷物品种进行鉴别。燕麦中不含谷蛋白,常混有富含谷蛋白的异种粮粒,Erkinbaev等采集了1 872 个混合谷物900~1 700 nm波长处的近红外光谱,结合主成分分析法和PLS判别分析法对燕麦和其他富含谷蛋白谷物进行鉴别分析。结果表明,燕麦与其他富含谷蛋白的谷物相比,吸收带的差异主要与1 200 nm和1 450 nm波长附近的C—H、N—H和O—H基团的振动有关,因此,仅使用5 个关键波长(1 069、1 126、1 189、1 243、1 413 nm)条件下建立的模型具有良好的预测准确率(99%),能精准地从富含谷蛋白的谷物中鉴别出燕麦籽粒。有机农业中不使用合成化肥和杀虫剂,与传统农业种植出的作物在营养成分上存在差异,Xiao Ran等采集了48 份水稻(26 份有机水稻、22 份普通水稻)的近红外光谱,采用PLS对水稻的近红外光谱分析,并建立水稻品种的鉴别模型。结果表明,有机水稻和传统水稻中与蛋白质含量相关的N—H基团在5 628 cm-1和6 394 cm-1的吸收峰和与纤维素和淀粉含量相关的C—H基团在6 250 cm-1和7 518 cm-1的吸收峰存在显著差异,且鉴别模型的决定系数为0.843 0,RMSECV为0.198 2,证明近红外光谱技术可以快速准确鉴别水稻的品种。Wu Yixuan等通过近红外光谱技术结合支持向量机、PLS判别分析和反向传播神经网络法建立了5 种小麦品种(1 种糯小麦、3 种部分糯小麦、1 种非糯小麦)的判别模型,其中,支持向量机模型判别准确率(98.51%)高于其他两种模型。不同地区生产的谷物往往会受到土壤元素条件和质量的影响,导致谷物营养成分含量不同,近红外光谱也可以通过区分谷物溯源地对谷物品种进行鉴别。Kabir等采用可见光和近红外光谱技术分别结合K-最近邻法、线性判别分析法、逻辑回归法、随机森林法和支持向量机法,对中国16 个地区小米品种的溯源地建立鉴别模型,5 种模型的F-分数均大于98%,随机森林法最高(100%)。Schütz等采用傅里叶变换近红外光谱技术结合优化支持向量机法建立了101 份来自5 个国家玉米溯源地的一个判别模型,准确率为95%。由以上研究可见,近红外光谱技术对谷物中异种粮粒、谷物品种以及谷物溯源地的鉴别需根据谷物种类选择最优模型,因此大多数研究建立的模型仅适合单一品种的鉴别,具有一定的局限性。
尽管重金属元素在近红外光谱中没有吸收带,但是通过其与有机物的螯合作用,可间接反映重金属的含量。Miao Xuexue等采用近红外光谱技术扫描了825 份大米样品,结合PLS对水稻的近红外光谱进行分析,研究发现水稻中镉与直链淀粉、淀粉和蛋白质的结合实现了近红外光谱技术对水稻镉的定量分析,模型的RMSEP和相关系数分别为0.213 3和0.902 0,证明近红外光谱技术对水稻重金属检测具有可行性。甲基毒死蜱是一种常用于去除水稻虫害的有机磷农药,在近红外光下有特定的吸收峰。Rodriguez等采集了100 g大米样本在950~1 650 nm波长处的近红外光谱,结合PLS建立糙米、脱壳大米和抛光大米中甲基毒死蜱含量的定量模型,决定系数均大于0.78,表明近红外光谱技术具有检测谷物农药残留的潜力,但精确度仍需进一步提高。
5 结语

近年来,近红外光谱技术在谷物检测中的应用已经显示出巨大的优势和潜力。它是一种快速、无损、高效的分析技术,能够准确测定谷物的营养成分、理化性质和霉菌污染。近红外光谱技术对谷物营养成分的定量检测适合采用PLS、支持向量机以及MLR等多种模型,主要根据谷物的品种和检测的营养成分进行选择;近红外光谱技术对谷物理化指标的检测多采用PLS模型;对谷物霉菌污染的鉴别分析适合采用PLS判别分析模型。此外,根据近红外光谱技术对谷物中营养成分定量检测的适用性,近红外光谱技术还可以采用PLS模型和支持向量机模型分析谷物中脂肪酸的含量,以及采用判别分析法根据谷物储存产生的挥发性化合物对谷物新陈度进行鉴别;近红外光谱技术还可以采用PLS模型对谷物中异种粮粒和谷物品种进行鉴别;近红外光谱技术同时具有谷物重金属和农药残留检测的潜力。尽管近红外光谱技术具有多种优点,但其在建模方面往往花费时间较长,且检测的精准度依赖于模型的质量。为了更好地将该技术应用于谷物检测,今后可以进一步优化算法从而节省时间,建立更为优化的模型提高适用性和预测的精准度。

作者简介
通信作者

赵卿宇,中国农业大学食品科学与营养工程学院副教授,药食同源方向博士后,主要从事杂粮生物活性物质挖掘及功效评价、粮食储藏理论与加工技术、功能性食品开发等领域。主持国家自然科学基金青年基金1 项,中国博士后特别资助(站中)/面上基金2 项、横向项目2 项,参与国家自然科学基金面上项目、“十三五”“十四五”国家重点研发计划、国家现代农业产业技术体系等国家级项目7 项。参与发表学术论文50余篇,以第一/通信作者在《Food Hydrocolloids》《Food Chemistry》《Food Research International》等期刊发表SCI论文15 篇(ESI高被引1 篇),EI论文5 篇,中文核心3 篇,授权中国/美国发明专利21件,受理发明专利10 件;副主编杂粮中文专著1 部,参与《小米》《粟》国家标准修订;获北京市优秀毕业生、青海省科学技术进步奖二等奖,中国食品工业协会科学技术奖一等奖等。
第一作者

王子熙,本科毕业于西北农林科技大学食品科学与工程专业,研究生毕业于新加坡国立大学食品科学与人类营养专业,主要研究食品中的营养成分的功效、粮食中生物活性物质的挖掘及功效评价、功能性食品开发等领域。参与发表学术论文4 篇,以第一作者发表EI论文2 篇。
实习编辑:安宏琳;责任编辑:张睿梅。点击下方阅读原文即可查看全文。图片来源于文章原文及摄图网
近期研究热点




长按或微信扫码进行注册
为系统提升我国食品营养与安全的科技创新策源能力,加速科技成果向现实生产力转化,推动食品产业向绿色化、智能化、高端化转型升级,由北京食品科学研究院、中国食品杂志社《食品科学》杂志(EI收录)、中国食品杂志社《Food Science and Human Wellness》杂志(SCI收录)、中国食品杂志社《Journal of Future Foods》杂志(ESCI收录)主办,合肥工业大学、安徽农业大学、安徽省食品行业协会、安徽大学、合肥大学、合肥师范学院、北京工商大学、中国科技大学附属第一医院临床营养科、安徽粮食工程职业学院、安徽省农科院农产品加工研究所、安徽科技学院、皖西学院、黄山学院、滁州学院、蚌埠学院共同主办的“第六届食品科学与人类健康国际研讨会”,将于 2026年8月15-16日(8月14日全天报到)在中国 安徽 合肥召开。

长按或微信扫码进行注册
会议招商招展
联系人:杨红;电话:010-83152138;手机:13522179918(微信同号)


