一作解读 | JIA|河南农业大学陈锋教授团队在小麦抽穗期遗传位点解析方面取得新进展
- 2026-05-22 19:22:08
2026年2月10日,河南农业大学农学院陈锋教授团队在Journal of Integrative Agriculture在线发表了题为“Dissection of genetic loci modulating heading date in common wheat”的研究论文。该研究整合基因组、转录组和蛋白组等多维度数据,通过构建小麦全基因组重组景观、GWAS、QTL定位、重要基因eGWAS、翻译后修饰等手段挖掘了抽穗期相关基因并构建了调控网络,为培育气候适应型小麦新品种提供了新见解。
一、绘制小麦全基因组重组景观
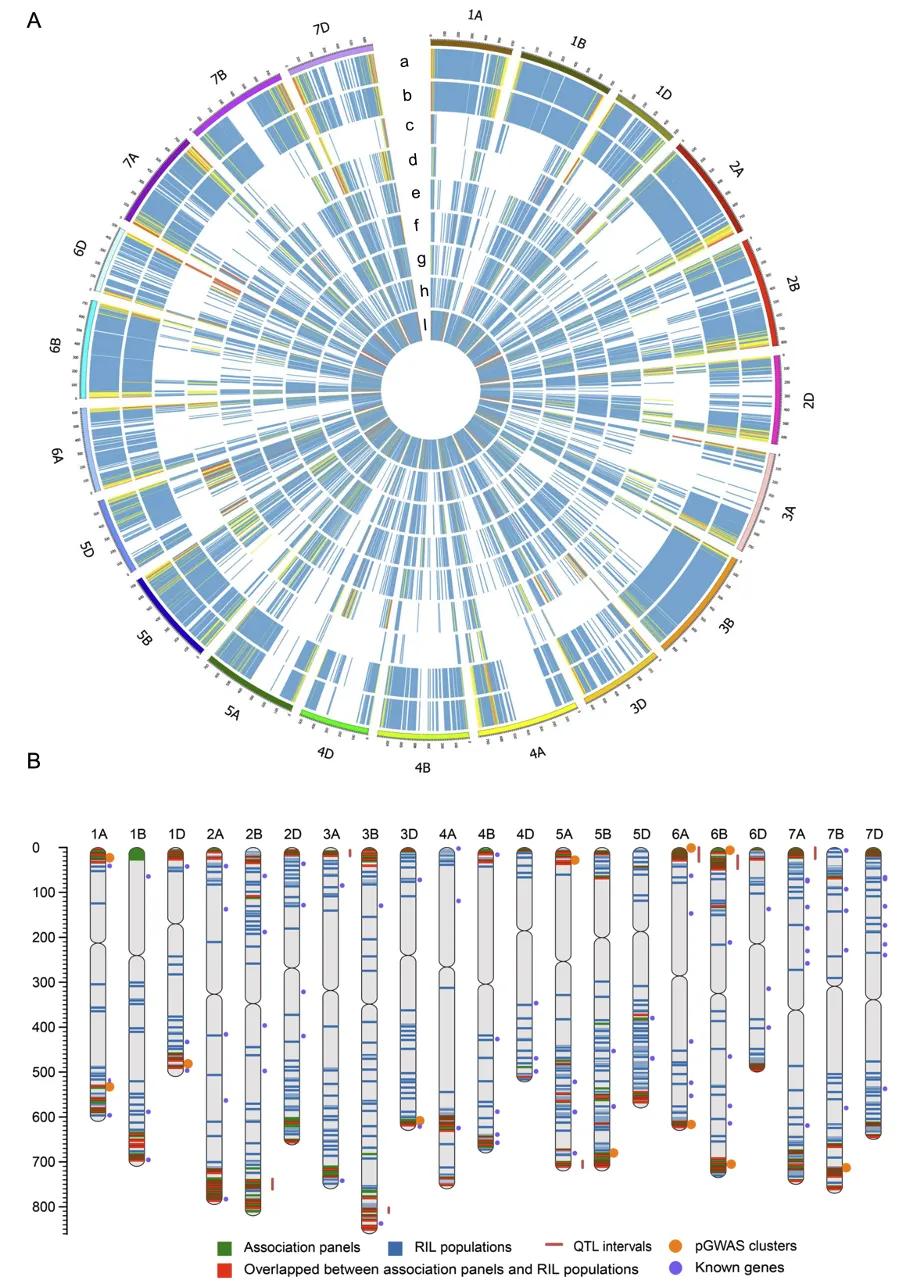
该研究在三个自然群体和六个双亲群体中系统鉴定了小麦重组事件,自然群体中共鉴定出97个重组热点区域,其中88个在不同遗传背景的双亲群体中稳定检测到(图1)。进一步研究发现,有261个与抽穗期相关的显著SNP、17个性状关联簇都位于以上热点区域内。因此,针对这些区域进行选择,可以有效地打破不良基因的连锁累赘,促进优良等位基因的重新组合,从而提高育种效率。
二、多方法挖掘调控抽穗期的遗传位点
pGWAS(表型关联分析)在多个环境中共鉴定到2223个显著SNP位点,其中53个为至少两个环境中都检测到的稳定SNP,关联13个候选基因。在双亲群体中共定位到21个控制抽穗/开花期的QTL。其中,位于2D染色体上的QHD.hau-2D.1效应最强,可解释高达31.2%的表型变异(图2)。
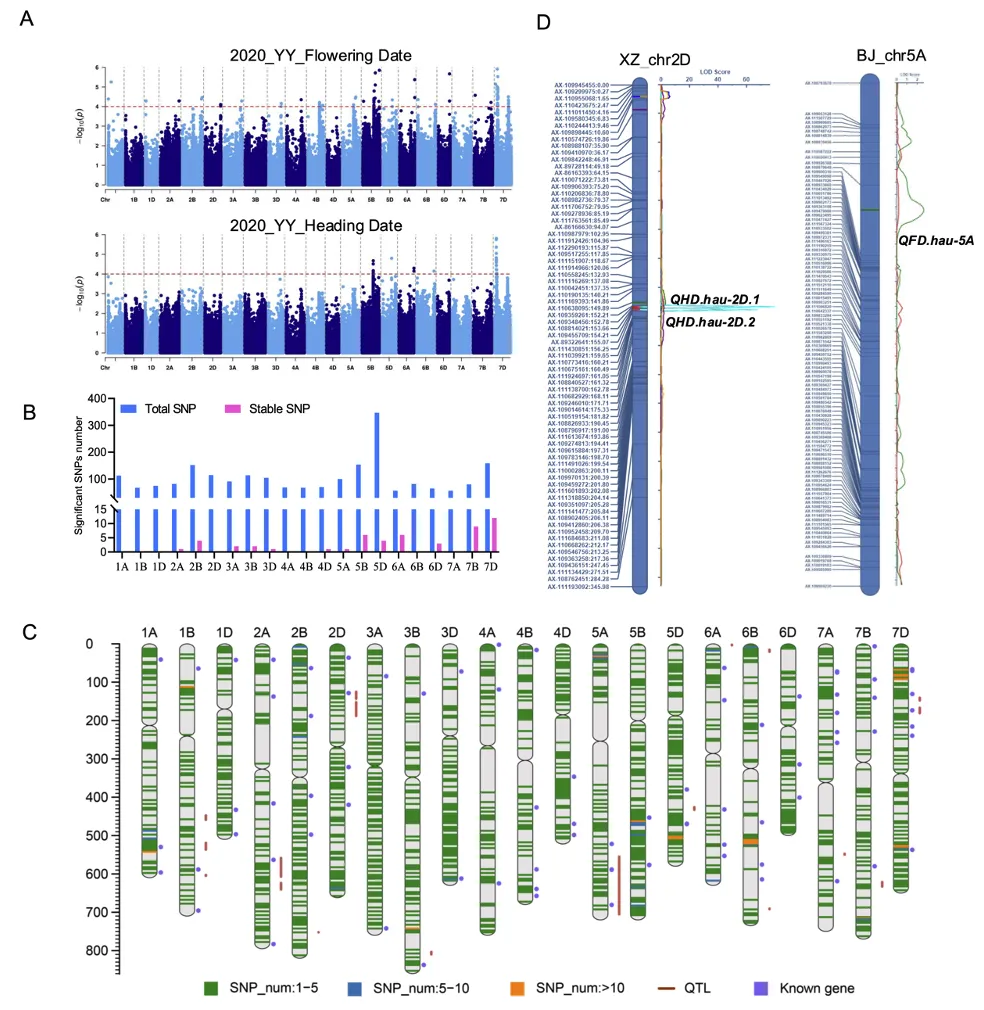
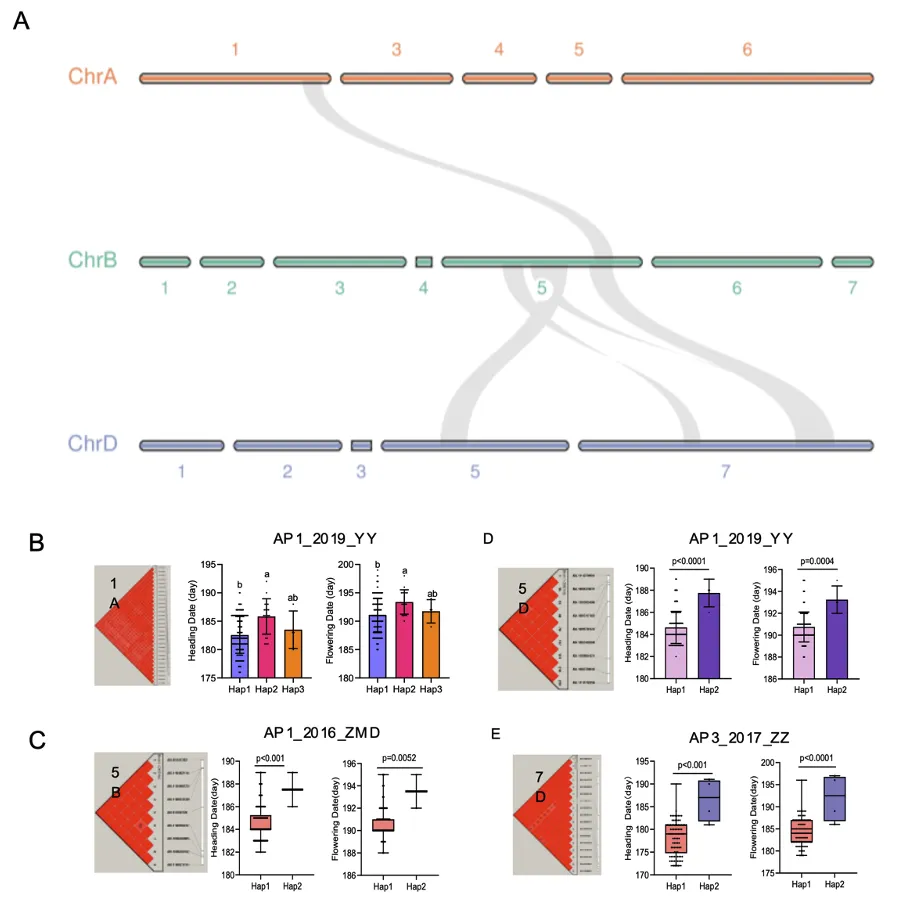
研究进一步对显著区间进行了共线性分析,鉴定到了5对跨染色体的同源区间,并挖掘到了能显著改变抽穗期的优势单倍型。7D_Hap1使抽穗和开花分别提前8.7天和8天,5B_Hap1使抽穗和开花提前3天。这些发现不仅揭示了基因组进化中的保守调控模块,更为分子标记辅助选择提供了具体靶点(图3)。
三、从“表达调控”维度发现新枢纽基因
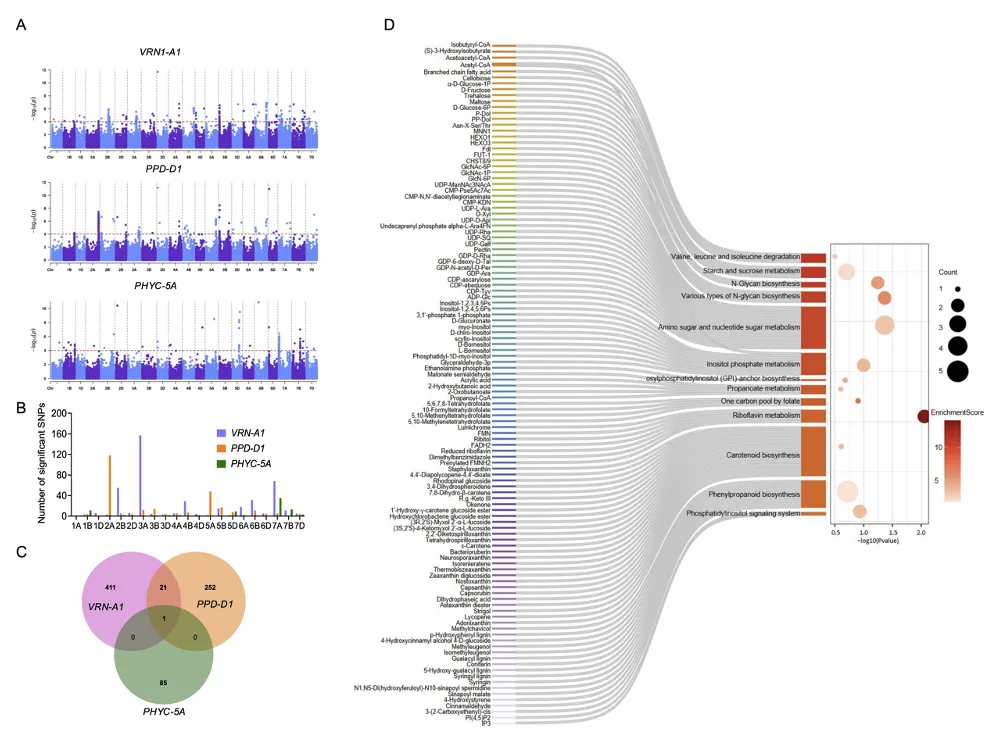
研究进一步对抽穗调控网络的核心基因(VRN-A1、PPD-D1、PHYC-5A)进行了表达水平上的全基因组关联分析(eGWAS)。共挖掘出三个基因的307个潜在的转录调控位点,丰富了抽穗期的调控网络。其中TaANT1(编码线粒体蛋白)同时与三个核心基因表达都相关,其TaANT1-D1b单倍型(携带提前终止密码子)可导致抽穗开花延迟2天。TaDRS1(注释为RNA解旋酶)同时被pGWAS和eGWAS鉴定到,其TaDRS1-A1b单倍型(移码突变)可使抽穗开花提前1天。以上两个基因位于调控小麦抽穗期的关键节点,为小麦抽穗期性状的遗传改良提供了重要的基因资源(图4)。
因此,该研究通过整合基因组重组景观、遗传定位、共线性分析和表达调控网络等构建了小麦抽穗期遗传网络的多维框架,为通过分子设计育种培育适应未来气候的高产、稳产小麦品种奠定了坚实的理论基础。河南农业大学陈锋教授和孙丛苇副教授为共同通讯作者,博士生郑跃婷和硕士生井震海为共同第一作者。该研究获得国家重点研发计划、河南省科技计划联合基金项目、国家自然科学基金、河南高校重点科研项目资助。