一作解读 | TAG | 新疆农业大学团队利用GWAS解析小麦条锈病抗性位点
- 2026-06-05 04:02:21
研究背景
小麦条锈病由Puccinia striiformis f. sp. tritici(Pst)引起,严重影响小麦的产量和质量。该病在全球范围内广泛传播,尤其在中国,每年都对小麦生产造成重大影响。随着抗性品种的替代,条锈病的致病菌不断进化,新病种不断出现,导致部分小麦品种失去抗性。因此,识别和应用新的抗性基因,尤其是耐久抗性基因,已成为提高小麦生产稳定性和保障粮食安全的关键。

目前已有87个正式命名或临时指定的条锈病抗性基因(Yr基因),但仅Yr5、Yr15、Yr18等少数基因被成功克隆并应用于抗病育种,多数抗性相关数量性状位点(QTL)尚未被开发利用。育种实践中育种家过度依赖少数已验证的抗病基因,导致抗病基因资源单一,而不同麦区的小麦品种是经长期人工和自然选择的遗传资源,适配本地环境,可能蕴含大量未被发现的抗病基因,是挖掘新抗性资源的重要载体。
全基因组关联分析已在水稻、玉米等多种作物中成功应用,2006年首次被用于小麦籽粒和面粉品质相关QTL分析,验证了其在小麦育种研究中的有效性。后续研究中,关联分析被广泛用于小麦产量相关农艺性状、条锈病抗性等分析,如研究者通过关联分析构建了小麦条锈病抗性基因全景图、定位了多个产量相关QTL,证明该技术是挖掘小麦新遗传位点的有效手段,为本次研究采用关联分析分析小麦条锈病抗性奠定了方法学基础。
研究结果
1.表型鉴定:筛选出优质抗锈种质,抗性性状遗传力高
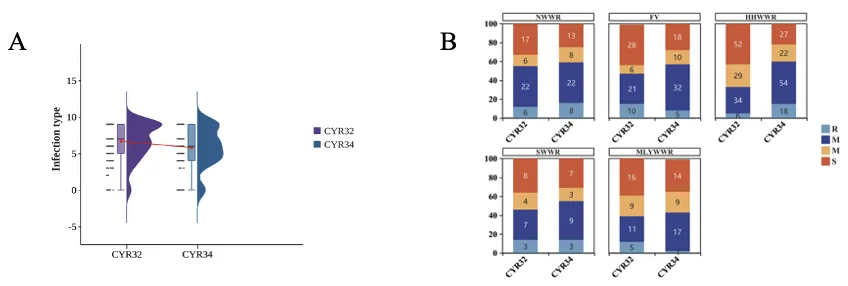
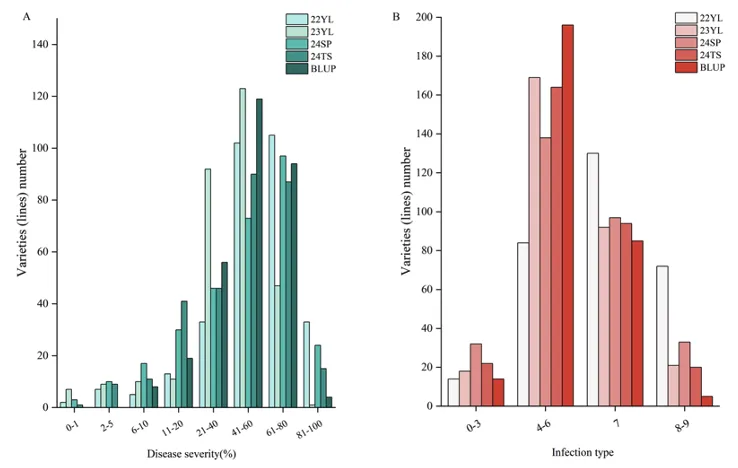
苗期抗性:300份材料对优势小种CYR32、CYR34的侵染型呈连续分布,41.7%抗CYR32、56.3%抗CYR34,27%对两个小种均抗;16份材料表现出全生育期抗性(ASR),整体苗期抗性水平较高(图1、2)。
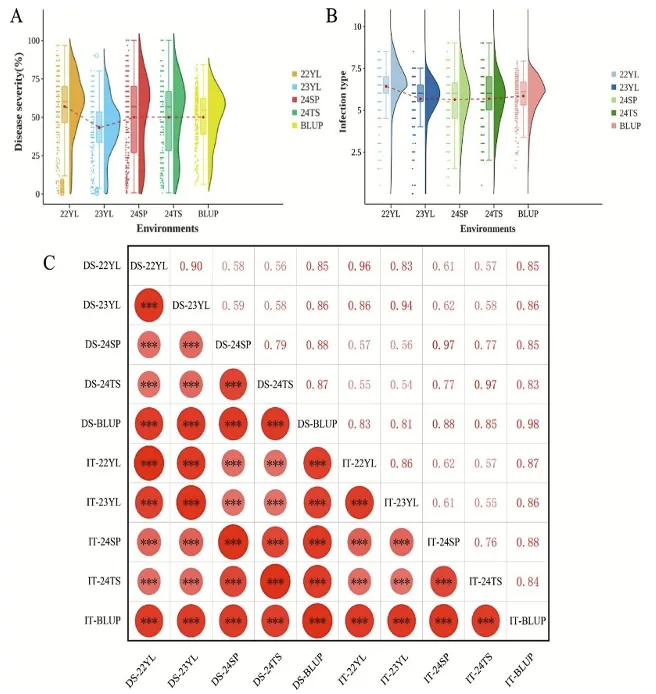
成株期抗性:四年四点(22YL、23YL、24SP、24TS)鉴定显示,不同环境下抗病性存在显著变异,但条锈病严重度(DS)和侵染型(IT)的广义遗传力均达0.89,表明抗性性状主要受遗传控制;多环境综合筛选出76份成株期稳定抗锈材料,62%左右材料在23YL、24SP环境中表现抗性(图2、3)
综合抗性:26份材料为全生育期抗性、24份为成株期抗性,这些抗源为抗病育种提供了核心亲本材料。
2.已知抗病基因检测:基因分布不均,存在未知抗性资源
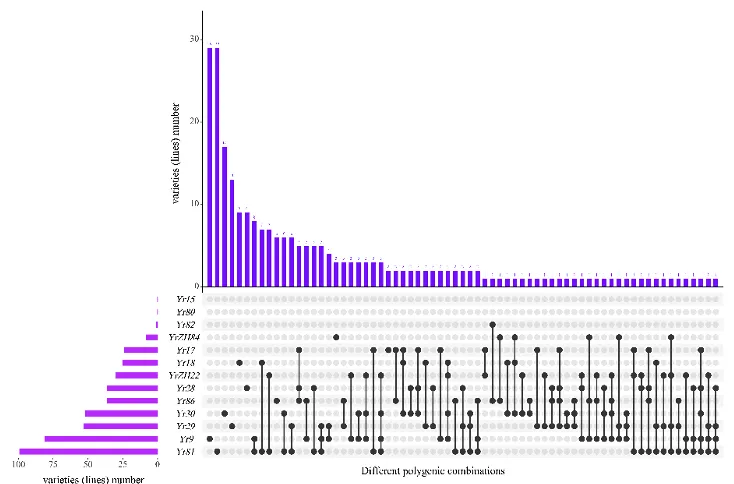
对13个已知Yr基因的分子检测发现,Yr15、Yr80在供试材料中未被检测到,Yr82分布频率仅0.33%;Yr81、Yr9、Yr29/Yr30为分布频率较高的基因(图4)
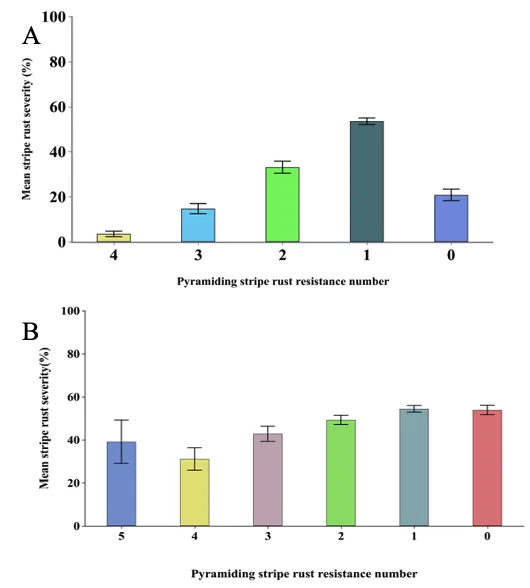
44%的材料聚合了2~5个抗锈基因,基因聚合数与病害严重度呈负相关;16%的材料(48份)不含检测的13个Yr基因,但其中川麦41等材料抗性良好,推测含有未知的有效抗锈基因(图5)
3.SNP标记与群体结构:D基因组多态性最低,材料分为3个亚群
经质量控制获得17187个高质量SNP标记,A、B、D基因组分别占42.82%、43.97%、13.21%,D基因组的遗传多样性和多态性信息含量(PIC)最低(全基因组平均PIC=0.25);标记平均物理间距0.82Mb,3B染色体物理长度最长,4D标记数量最少。
群体结构分析显示,300份材料可分为3个亚群,亚群1以黄淮麦区、北方麦区为主,亚群2以黄淮麦区、长江中下游麦区为主,亚群3含43.90%国外品种;全基因组连锁不平衡(LD)衰减距离为1.72Mb,为后续QTL定位的区间划分提供依据。
4. QTLs定位与分析:挖掘出20个苗期、12个成株期抗性QTL
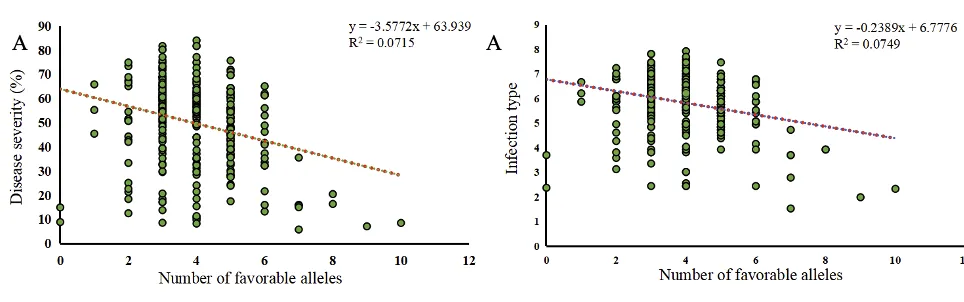
通过GWAS分析,研究共识别出20个与种苗抗性相关的数量性状基因座(QTLs),以及12个与成株抗性相关的QTLs。这些QTLs分布在多个染色体上,解释了条锈抗性表型变异的0.01%至20.85%。此外,研究揭示了有利等位基因在提高抗病性方面的关键作用,表明抗性基因位点的数量与小麦抗病性呈显著正相关(图6)。这些QTLs的发现为进一步解析小麦抗条锈的遗传机制提供了基础,有助于抗性基因的定位和功能研究。
5.候选基因与单倍型分析:筛选出12个抗病候选基因,Hap2显著提升抗性
在稳定抗性位点区间内筛选出12个与条锈病抗性相关的候选基因,主要为NBS-LRR类抗病蛋白、RPM1、细胞色素P450、锌指蛋白等,均参与植物病原菌防御反应。对核心位点QYr.xjau-3D、QYr.xjau-6B.1进行单倍型分析,发现QYr.xjau-3D存在Hap1和Hap2两个单倍型,Hap2材料的病害严重度显著低于Hap1,为优异抗锈单倍型;QYr.xjau-6B.1的Hap2仅在IT性状上表现出抗性差异(图7)。
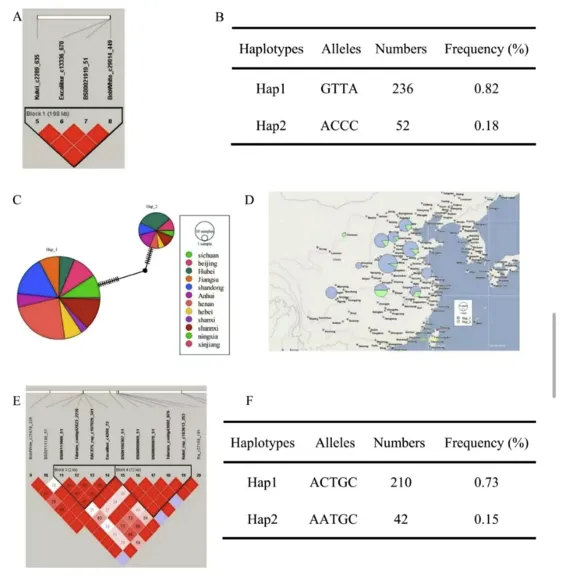
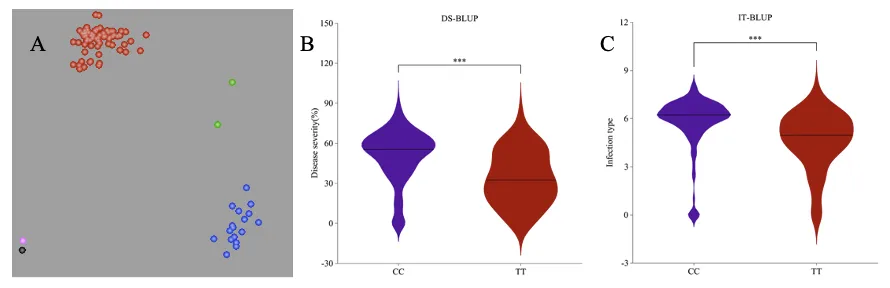
6.分子标记开发:成功开发并验证KASP功能标记
本研究基于GWAS结果开发了针对SNP位点Kukri_c2289_635的KASP标记,证明该标记可以有效地区分不同的小麦基因型。通过在小麦品种中进行基因分型,验证了该标记在分子育种中的应用价值(图8)。研究还发现,不同等位基因的表现差异在病害严重度和感染类型上具有显著差异,为未来的分子辅助育种提供了可靠的工具。
总结与展望
本研究通过全基因组关联分析(GWAS),系统解析了小麦条锈病抗性的遗传基础,成功识别出多个与抗性相关的数量性状基因座(QTLs)和新抗性位点。研究筛选出稳定抗锈种质,开发了可用于分子辅助育种的KASP功能标记,为小麦条锈病抗性基因定位、分子标记开发及抗病品种筛选提供了理论依据与实践指导。未来将进一步验证QTL功能、优化抗性基因组合,通过分子育种培育更精准多样的抗病品种,以应对条锈病变异与环境挑战。
研究团队与资助
上述研究成果由新疆农业大学农学院博士研究生张飞飞与已毕业硕士生王荣并列第一作者,程宇坤副教授和耿洪伟教授为通讯作者,在《Theoretical And Applied Genetics》期刊发表,题目为“Unveiling the genetic architecture of stripe rust resistance in wheat: a region specific GWAS in Xinjiang, China”的研究论文。该研究得到伊犁谷地主要作物病虫害绿色防控技术研发项目(2022B02015-3)、中国博士后科学基金 (2021MD703887)和新疆维吾尔自治区重大科技专项项目(2024A02003-2)项目资助。