科研、项目合作:panp6600 (注明来意,清北硕博团队专注于AI for Science自研大模型,接受天使轮投资,欢迎投资者咨询)
————————————
本文内容独家整理,盗用必究
蛋白质功能的精确解析一直是生物信息学领域的核心挑战。孟加拉农业大学计算机科学与数学系团队在Sifullah Mahmud Sefa和Machbah Uddin教授的带领下,开发了一款名为ProteoMapper的创新计算框架,实现了蛋白质结构域(domain)和短线性基序(motif)的整合分析。该工具不仅突破了传统分析方法的局限,还首次提出了定量化评估基序-结构域空间关系的创新指标,为功能蛋白质组学和比较基因组学研究提供了全新的分析视角。
为何需要整合分析蛋白质域与基序?
蛋白质功能的实现依赖于保守结构域与调控基序的协同作用。保守结构域为蛋白质提供稳定的结构框架,使催化活性、分子识别和结构完整性得以实现;而短线性基序则编码紧凑的调控逻辑,如磷酸化位点、降解信号和瞬时蛋白-蛋白相互作用界面。这两类元素共同塑造了蛋白质在不同细胞环境中的行为模式。
然而,当前的蛋白质分析工具存在明显的分离性问题。基于轮廓隐马尔可夫模型(profile Hidden Markov Model, HMM)的工具如HMMER和InterProScan能够通过序列-轮廓比对准确识别保守结构域,但它们不支持用户自定义基序检测,也无法定量评估基序与结构域的空间关系。相反,专注于基序的资源如ScanProsite、MEME、ELM和EMBOSS Fuzzpro能够检测线性序列模式,但缺乏整合的结构域背景、比对级别的保守性分析和标准化的嵌入度量指标。
研究团队指出,确定特定序列基序是否通过嵌入保守结构域而受到进化约束,还是作为灵活的调控元件独立进化,这一区分具有重要的生物学意义。位置保守且结构域嵌入的基序更可能直接参与核心蛋白质机制,而位于非约束区域的基序则可能编码调控或谱系特异性功能。
ProteoMapper的核心技术架构:双重指标体系
ProteoMapper的技术创新集中体现在两个互补的发现指标上。第一个指标是位置保守性评分(positional conservation scoring),它识别在比对坐标上完全相同位置出现的基序,且该基序必须在用户定义比例的序列中出现(默认阈值为60%),这表明该基序受到纯化选择的约束。这一指标不同于简单的频率统计,它捕获的是位置特异性,这对于区分功能约束基序和耐受性序列模式至关重要。
第二个指标是基序-结构域覆盖分数(Motif-Domain Coverage Score, MDCS),这是研究团队提出的定量化创新指标。MDCS的数学定义为:
MDCS值在0到1之间变化,其生物学解释非常直观:MDCS=1表示基序完全嵌入结构域内部,0<MDCS<1表示基序跨越结构域边界,MDCS=0则表示基序位于注释结构域之外。当基序在序列中多次出现或与多个结构域重叠时,ProteoMapper保留每个结构域登录号观察到的最高MDCS值,以总结最强的基序-结构域关联。
从技术实现角度看,整个分析流程展现了严谨的工程设计思想(见图1:工作流程图)。
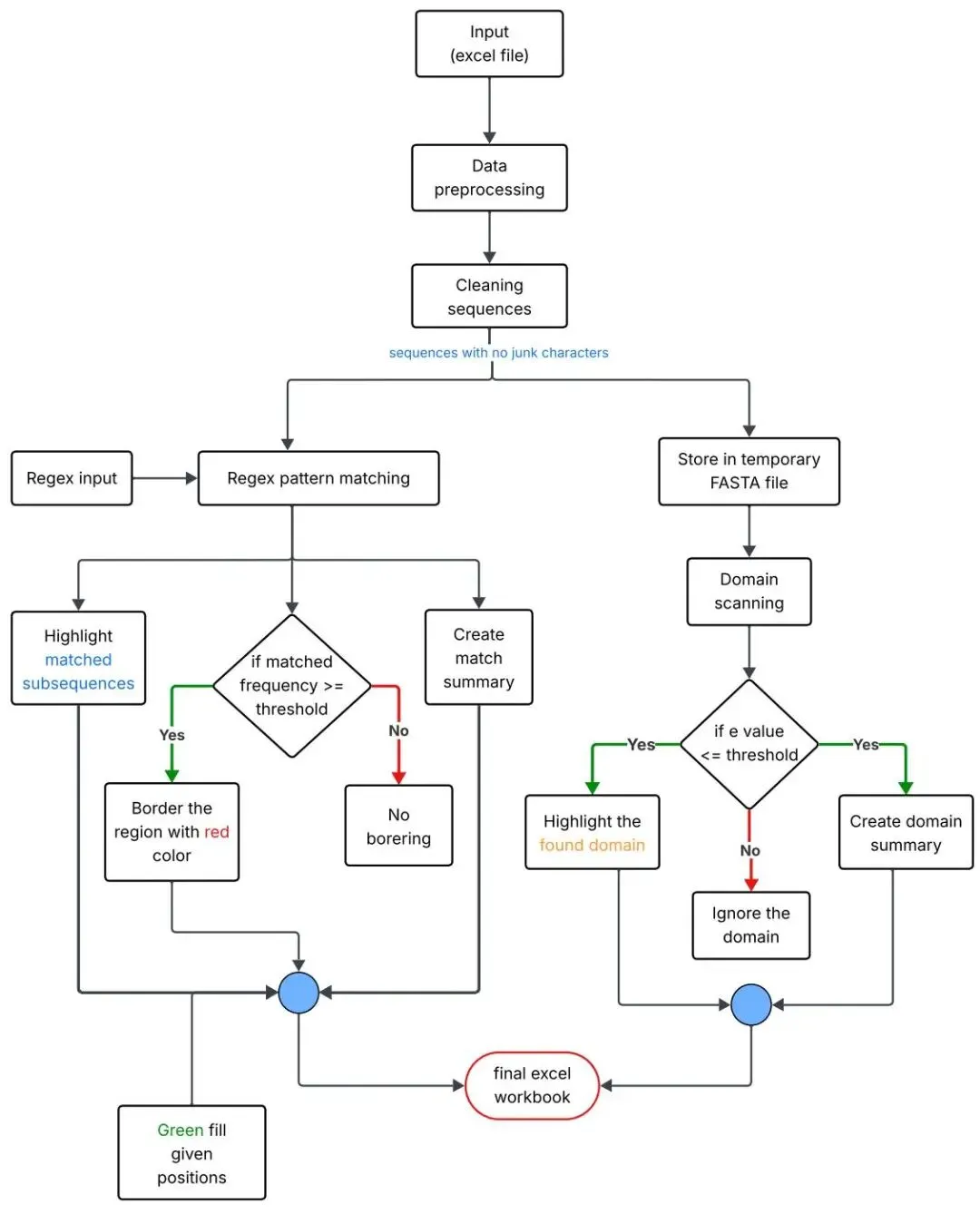
图1展示了ProteoMapper的完整分析流程,包括输入Excel格式的序列比对文件、自动检测表头、序列清洗与标准化、并行执行基序匹配与结构域预测、以及生成多表格Excel输出报告。
数据预处理:从Excel到可分析序列的精细化处理
ProteoMapper采用Excel格式(.xlsx)作为输入文件,这一设计体现了对实验生物学家工作流程的深刻理解。Excel允许将基因名称或标识符与对应的蛋白质序列存储在同一行中,避免了元数据和序列分别维护时的同步问题。如果序列包含gap字符(例如"-"),电子表格网格使得比对在人工检查时易于查看。输入文件至少需要包含两列:Gene Name/Gene ID(存储序列标识符)和Protein Sequences(包含蛋白质序列)。
序列清洗与标准化过程遵循严格的操作规范:首先处理FASTA格式,如果序列以">"开头,则移除该符号并记录原始表头以保留来源信息;其次移除无效字符,删除不属于20种标准氨基酸(A, C, D, E, F, G, H, I, K, L, M, N, P, Q, R, S, T, V, W, Y)的任何字符;最后生成两种表示形式——显示视图保留比对gap("-")用于可视化和比对检查,匹配视图移除gap和任何剩余非氨基字符以产生适合模式匹配和基序搜索的连续序列。
这种双重序列表示策略的设计十分巧妙。多序列比对算法如MAFFT会引入可变的gap分布模式,这些gap模式和标准化处理会影响序列间的比对质量。通过同时维护显示视图和匹配视图,系统确保下游基序搜索和结构域注释操作在干净、一致的序列上进行,同时保留了原始比对信息供用户参考。
基序匹配的并行化算法实现
ProteoMapper支持使用用户定义的正则表达式进行灵活的蛋白质基序检测。与固定模式匹配方法不同,正则表达式引擎赋予研究人员对想要搜索的基序模式的完全控制权。用户可以定义特定或简并基序,例如磷酸化位点(如)或标准数据库中不存在的家族特异性签名。修饰位点如N-糖基化()也可以被识别。
基序匹配引擎运行在两种模式下。对于少于100个序列的数据集,系统使用串行执行;对于更大的数据集,它将计算分配到多个工作进程中。用户可以直接通过图形界面设置进程数量。算法1详细描述了基序匹配和保守性高亮的完整流程:
算法分为四个阶段:阶段1:模式准备,从GUI提取模式并移除空条目,预编译所有模式并支持不区分大小写的匹配;阶段2:执行模式选择,如果序列数则设置为串行模式,否则设置并使用并行模式;阶段3:基序匹配,根据模式将数据集分块,对每个序列生成无gap和有gap两种形式,构建位置映射(无gap坐标→有gap坐标),对每个模式在无gap序列中检测匹配,通过映射将匹配坐标转换为有gap位置,记录匹配位置并增加计数;阶段4:保守性高亮,计算,统计每个匹配列范围的频率,对频率的范围在所有行的相应列应用红色粗边框。
保守性阈值参数的设置体现了进化生物学的理论基础。用户可以指定必须包含给定基序的最小序列百分比,如果基序在同一位置边界内出现,则将其分类为该范围内的保守基序。默认阈值为60%。满足或超过此水平的基序在输出中用红色边框突出显示,这种可视化策略使得研究人员无需手动检查即可快速识别高度保守的基序位置。
基于HMMER的保守结构域并行预测
ProteoMapper通过并行执行多个hmmscan进程实现了对大规模序列集的高效处理。在该模式下,多个hmmscan进程同时运行,每个进程扫描输入序列的不同子集,所有进程的结果随后合并到单个输出文件中。
算法2展示了并行结构域检测的完整流程:首先初始化临时目录并设置总序列数;然后将个序列划分为num_processes个分块,计算;对每个进程,提取分块其中,生成独立的hmmscan进程,将分块写入FASTA文件,运行hmmscan命令hmmscan --domtblout out_i pfam_db fasta_i,解析domtblout输出并过滤满足的命中,将过滤后的命中保存到临时文件;等待所有进程完成后,读取所有临时文件并合并结果,清理临时文件和目录,将所有结果写入hitdata.txt。
结构域在Excel中的高亮显示采用了精心设计的可视化策略。系统生成交互式结构域注释,包括视觉注释和嵌入元数据两个层面。视觉注释层面,对domtblout中字段17-18预测的结构域边界内所有残基位置应用橙色填充(如算法3所示)。嵌入元数据层面,为每个结构域的起始位置生成动态单元格注释,包含:结构域名称(来自domtblout字段22+)、登录号(字段1)、坐标(字段17-18)以及E值和比特分数等统计指标。
需要特别强调的是坐标系统的设计考量。注释中实现的坐标(起始-结束位置)不是根据HMMER的无gap序列编号,而是基于包含"-"的比对蛋白质序列计算的。这确保了用户在查看比对视图时,结构域边界的标注与视觉显示完全一致,避免了坐标系统转换带来的混淆。
MDCS指标:量化基序与结构域的空间关系
基序检测和结构域注释通常作为独立分析进行,但某些短线性基序和保守结构域在蛋白质结构或序列中的位置关系能够提供重要的生物学见解。为支持这种解释,ProteoMapper计算基序-结构域覆盖分数(MDCS),这是一个描述基序与预测蛋白质结构域之间空间关系的定量度量。
对于同一序列中的每个基序出现和每个重叠的Pfam结构域,MDCS的数学定义为:
MDCS值的解释具有明确的生物学含义。值为1表示基序完全包含在结构域内,0到1之间的值表示与结构域边界的部分重叠,值为0表示基序位于注释结构域之外。当基序在序列中多次出现或与多个结构域重叠时,ProteoMapper为每个结构域登录号保留观察到的最高MDCS值,以总结最强的基序-结构域关联。
MDCS计算使用从hmmscan结构域预测得到的无gap序列坐标,确保与Pfam注释的一致性。结果在输出Excel文件的专用MDCS Summary工作表中报告,列出序列索引、基序模式、关联的结构域登录号、MDCS值和定性解释。通过以数字和易于过滤的形式总结基序-结构域嵌入,MDCS使用户能够快速区分可能是核心结构域功能的一部分的基序与出现在结构域边界或保守结构域之外的基序。
这一信息补充了基序保守性和频率分析,为下游生物学解释提供了额外的背景层,而不会增加大量的计算开销。
用户界面与输出结构:可视化分析的完整解决方案
运行项目代码后,显示的界面(图2)为用户提供了直观的平台,用于输入蛋白质序列比对、配置参数(如正则表达式模式、保守性阈值和HMMER选项)并可视化结果。
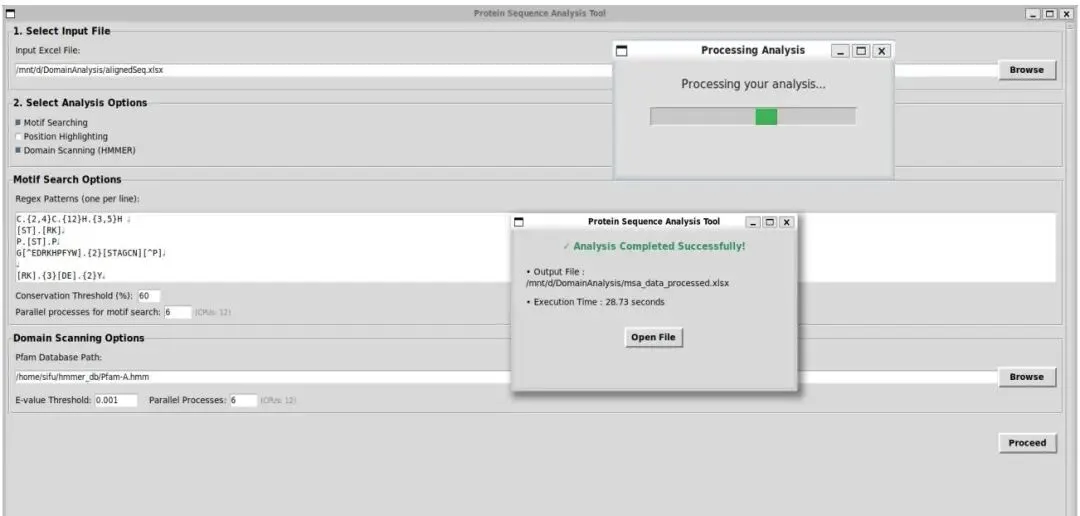
图2展示了集成计算工具包的用户界面,显示输入字段、处理标签和完成标签,整个界面设计简洁明了,即使是没有编程经验的实验生物学家也能轻松上手。
ProteoMapper处理后生成一个整合所有分析的多表格Excel工作簿(图3)。输出结构的设计充分考虑了用户的分析需求:
第一个工作表包含完整的比对矩阵。基于正则表达式的基序匹配以天蓝色显示。在≥60%(本测试中的阈值,用户可调)的序列中出现基序的列接收粗红色边框,无需手工检查即可突出高度保守的基序位置(图3D)。用户定义位置高亮功能允许用户指定的任何比对列(空格分隔的数字)在所有行中填充亮绿色,实现已知功能或变异位点的快速视觉映射(图3D)。
Match Summary工作表提供自动生成的表格,列出每个用户定义的正则表达式模式、其总匹配计数以及在比对中检测到的所有位置跨度。列级频率有助于识别重复或保守的基序区域(图3C)。
Domain Highlights工作表是比对的副本,带有从并行hmmscan扫描获得的Pfam结构域(本测试中E值)。检测到的结构域以橙色显示。每个结构域块包含嵌入的Excel注释,包含结构域名称、登录号ID、比特分数、E值和条件E值,直接在表格中提供完整的HMMER元数据(图3B)。
Domain Summary工作表提供所有检测到的结构域的表格摘要,包括E值、条件E值和比特分数。E值表示预期的假阳性数量,较低的值表示更高的置信度,而比特分数提供匹配质量的对数标度度量(图3E)。
MDCS Summary工作表报告每个检测到的基序出现的基序-结构域关系表。对于每个序列和基序模式,该表列出了每个重叠Pfam结构域(通过登录号ID报告)观察到的最高MDCS值,以及定性解释(例如,完全嵌入或部分重叠)。该摘要能够快速评估基序是否一致嵌入保守结构域边界内,正如ERD6-like蛋白案例研究所示(图3A)。
 A表格内容
A表格内容图3展示了ProteoMapper在代表性数据集上的输出。图中清晰呈现了:(D) 第一个工作表显示天蓝色基序匹配和保守列上的红色边框;(C) Match Summary表格;(B) Domain Highlights表格,带有橙色Pfam结构域和可悬停元数据;(E) Domain Summary包含HMMER统计数据;(A) MDCS Summary展示基序-结构域嵌入关系。
案例研究1:Brassica rapa的PLATZ转录因子结构域检测验证
为评估蛋白质分析工具的准确性,研究团队使用了Azim等人报道的24个来自Brassica rapa L.的PLATZ转录因子蛋白(BrPLATZ1-BrPLATZ24)的已发表数据集。原始研究使用SMART数据库识别了这些蛋白质并分析了它们的保守结构域,数据集包括PLATZ(PF04640)、同源框(PF00046)和B-box锌指(PF00643)等多个结构域。
研究团队将该工具应用于相同序列,使用HMMER(hmmscan)与Pfam-A数据库,采用E值阈值0.001和四个CPU核心。结果保存在hitdata.txt文件中,并以表1的形式呈现,记录了所有显著的结构域命中。
表1对比了SMART和ProteoMapper检测到的PLATZ和同源框结构域范围
(表格内容较长,此处仅展示部分)
ProteoMapper以高精度再现了大多数报告的结构域注释。对于PLATZ结构域(PF04640),23个报告命中中有22个完全匹配,例如BrPLATZ1(77-148)和BrPLATZ18(133-204)。一个蛋白质BrPLATZ17显示较短的匹配(74-98而不是74-127)。两种分析都未在BrPLATZ3中检测到任何PLATZ结构域。对于同源框结构域(PF00046),该工具仅在BrPLATZ3(181-234)中检测到它,与报告范围(180-235)非常接近。
除了结构域范围,ProteoMapper还提供了详细的指标,如比特分数(PLATZ命中的范围为28.3到111.0)和E值(全部),确认了检测的统计显著性。输出文件hitdata.txt还包括条件E值和结构域描述,供进一步验证。
关于B-box锌指结构域的差异体现了不同数据库策略的影响。SMART报告了24个BrPLATZ蛋白中有15个可能存在B-box锌指结构域(PF00643)。然而,该工具在默认E值阈值(≤0.001)下未检测到任何显著的B-box命中。Pfam和SMART都是领先的结构域数据库,但它们是独立策划的,对同一结构域使用不同的隐马尔可夫模型,这会影响检测灵敏度。基于Pfam的HMMER扫描应用基于精心策划的比对的更严格阈值,任何E值高于0.001的命中都会被自动排除。
案例研究2:番茄SlADF蛋白中ADF-H结构域的验证
Khatun等人进行了全面的全基因组分析,鉴定了番茄(Solanum lycopersicum)中的11个肌动蛋白解聚因子(ADF)基因。该研究根据不同器官和发育阶段的表达模式表征了这些蛋白质。通过SMART和InterPro工具确认所有11个蛋白质都含有ADF-H结构域(也描述为"Cofilin/原肌球蛋白型肌动蛋白结合蛋白",Pfam ID:PF00241),结构域跨度详见其研究的表2。
为验证该自定义工具的准确性和可靠性,研究团队重新分析了SlADF蛋白序列中的结构域存在。序列来自Khatun等人的补充材料,经过预处理(gap移除)后通过hmmscan对Pfam-A v35.0进行扫描,E值阈值为0.001。研究集中于前11个序列(11个SlADF)的结构域扫描结果,比较结构域位置和与Khatun等人的整体一致性。
表2对比了11个番茄SlADF蛋白中ADF-H结构域边界
(表格内容较长,此处仅展示部分)
ADF-H结构域(PF00241.26)在所有11个SlADF蛋白中以高置信度被检测到。结构域跨度重叠使用交并比(Intersection-over-Union, IoU)量化,定义为:
IoU为1表示完美对齐;值表示出色的重叠。
结构域边界与已发表跨度显示出强烈的一致性,平均IoU=0.94(范围:0.93-0.96),表明的位置重叠(表2)。起始位置在该工具中略早(平均偏移:-4.8个氨基酸),这可能是由于Pfam专注于核心保守区域而SMART注释范围更广。
该分析完全验证了Khatun等人的ADF-H结构域注释,检测率达100%,位置对齐接近完美(平均IoU 0.94)。边界的微小偏移反映了方法学差异(Pfam HMM与SMART),但不影响功能解释。
案例研究3:ERD6-like蛋白糖转运蛋白签名的保守性和结构域背景分析
ERD6最初在拟南芥(Arabidopsis thaliana)中被鉴定为早期脱水诱导基因,根据与已知单糖转运蛋白的序列相似性编码推定的糖转运蛋白。后续的进化分析表明,ERD6-like(ERDL/EDL)蛋白在陆生植物中形成保守的转运蛋白家族,同时表现出亚家族特异性序列分化。策划的数据库将ERD6-like蛋白注释为主要促进超家族(MFS)的成员,并报告存在两个PROSITE糖转运蛋白签名PS00216和PS00217。
研究团队使用ProteoMapper对来自拟南芥的17个ERD6-like/EDL蛋白(UniProt条目)进行了比对和分析。使用对应于PS00216和PS00217的正则表达式搜索两个PROSITE衍生基序。基序检测在无gap序列上执行,并投影回有gap比对进行可视化。使用HMMER对Pfam数据库进行结构域注释,采用严格的E值阈值。应用55%的保守性阈值,要求基序在17个序列中的至少10个相同比对位置出现才能分类为保守。
检测到两个糖转运蛋白签名,然而只有PS00217满足保守性标准。PS00217在10个序列(58.8%)的单个比对跨度(位置165-190)中被识别,因此被分类为保守的家族范围基序。相反,PS00216产生了更多的总匹配数(13),但这些分布在两个不同的比对区域(位置123-140和357-375),都未达到保守性阈值。因此,PS00216在55%阈值下未被分类为保守。
表3:使用55%保守性阈值在17序列ERD6-like比对中PROSITE糖转运签名的保守性分析
为进一步表征检测基序的结构背景,ProteoMapper计算了基序-结构域覆盖分数(MDCS),量化基序与预测Pfam结构域重叠的部分。接近1的MDCS值表示完全嵌入结构域内的基序,而接近0的值表示位于结构域边界之外的基序。因此,MDCS值接近1的基序表明它们可能是核心转运机制的组成部分,而不是外围或调控特征。
MDCS分析显示,PS00216和PS00217的出现主要完全嵌入预测的Pfam结构域边界内(MDCS=1)。尽管两个签名都是结构域嵌入的,但只有PS00217被确认为家族范围保守签名(58.8%频率),并确认了其作为整体转运机制组分的作用,而PS00216被识别为非保守基序。
这些结果与ERD6-like家族的已知生物学一致,该家族将转运蛋白特征与谱系或亚群特异性序列变异结合。保守性分析和基于MDCS的结构域背景评估共同展示了ProteoMapper如何在统一工作流程中整合基序检测、进化保守性和蛋白质架构解释。
性能评估:并行计算带来的显著提升
ProteoMapper使用150个比对的PLATZ蛋白质序列和八个生物学相关基序模式进行基准测试。这些模式包括:(i) (锌指C2H2),(ii) (PKC磷酸化位点),(iii) (脯氨酸定向磷酸化),(iv) (N-豆蔻酰化位点),(v) (酪氨酸激酶位点),(vi) (B-box锌指),(vii) (NPC1样富含半胱氨酸的结构域),以及(viii) (PLATZ特异性基序)。
设计了两个实验来评估可扩展性。首先,通过使用单个进程在50、100和150个序列上运行分析来测量运行时间如何随数据集大小增长。其次,通过使用1、2、4、6和8个进程运行完整的150序列数据集来评估多处理性能。
表4:ProteoMapper随序列数量和进程数量的性能扩展
性能表展示了随数据集大小和进程数量的高效扩展。在单进程模式下,运行时间与序列计数大致呈线性扩展,从10.9秒(50个序列)增加到29.0秒(150个序列)。基于HMMER的结构域扫描主导计算成本(约占总运行时间的93%),而正则表达式基序匹配仍然可以忽略不计(<0.3秒)。
为量化并行效率,加速比定义为:
其中表示一个进程的运行时间,表示个进程的运行时间。并行执行产生了显著改进,使用八个进程达到最大3.76倍加速比。超过四个进程后,由于多处理协调、临时文件I/O以及每个额外hmmscan实例将完整Pfam数据库加载到内存中的事实,并行效率逐渐下降。因此,加速比在1到4个进程之间从急剧上升到约,但此后趋于平稳,从6个进程到8个进程移动时仅产生边际收益(从到)。
结构域扫描从多处理中受益最大,从26.9秒(单进程)改进到5.7秒(八进程)近四倍。相反,基序匹配在所有配置中保持一致的低水平,表明无论并行化策略如何,模式识别任务的计算需求都很小。
技术优势与局限性:清晰的定位与未来方向
ProteoMapper的核心贡献在于建立了一个定量化框架,用于调查保守蛋白质结构域和短线性基序之间的空间和进化关系。跨三个家族52个蛋白质的验证展示了技术准确性(平均结构域边界交并比为0.94,ADF-H结构域检测率100%)和生物学洞察生成能力。
该工具与现有资源形成互补关系。InterProScan通过整合多个签名数据库进行大规模结构域注释方面仍然是最全面的平台,但需要命令行专业知识、大量计算资源,并生成不适合交互式解释的复杂输出格式。HMMER是基于轮廓HMM的结构域检测的标准,但其基于文本的输出需要额外的下游处理以支持整合分析。
在基序分析方面,ScanProsite提供方便的基于网络的策划PROSITE签名检测,但不支持结构域注释或大规模批量分析。EMBOSS Fuzzpro支持命令行模式匹配,但缺乏比对级别可视化和结构域背景解释。像Wregex及其后续版本这样的概率基序检测框架通过加权正则表达式和位置特异性评分矩阵为弱或简并基序提供改进的灵敏度,但这些方法需要策划的训练数据,并生成不太直观解释的连续分数。
ProteoMapper也存在一些局限性。目前不支持加权基序评分、基于PSSM的模型或保守性排序的基序发现,这可能限制对高度简并或新颖基序的敏感性。尚未实现对复杂多基序架构(如间距依赖的组合签名)的显式建模。包含基序的蛋白质的功能富集分析也超出了当前范围。此外,非常大规模的蛋白质组分析在高性能计算环境中可能由InterProScan或HMMER等命令行管道更有效地处理。
未来的发展将集中在可选整合加权基序评分同时保持可解释性,扩展多基序架构建模以捕获共进化间距约束,以及纳入功能富集分析。这些扩展旨在拓宽分析范围,而不损害可访问性或比对感知可视化。
结论
ProteoMapper为研究保守蛋白质结构域和短线性基序之间的空间和进化关系提供了一个定量框架。该工具利用多核并行处理的能力同时处理多个序列,用简单的小基序搜索来发现大结构域。通过整合基序检测、结构域注释、保守性分析和定量空间指标于统一工作流程中,ProteoMapper支持在功能基因组学、比较蛋白质分析和结构生物信息学中对蛋白质架构、调控组织和进化动力学进行可访问的研究。
该平台直接在Excel格式的多序列比对上操作,并生成可解释的多表格可视化输出,无需编程专业知识,支持可重现和迭代的假设检验。这种设计理念使得该工具特别适合实验生物学家使用,降低了生物信息学分析的门槛。
论文引用:
Sefa, S.M., Sarkar, J., Robin, A.H.K., and Uddin, M. (2025). ProteoMapper: Alignment-Aware Identification and Quantitative Analysis of Contextual Motif–Domain Patterns in Protein Families. Bioinformatics Engineering, Department of Computer Science and Mathematics, Bangladesh Agricultural University.
项目资源:
- GitHub代码仓库:https://github.com/sifullah0/ProteoMapper
- 测试数据集与输出示例:https://github.com/sifullah0/ProteoMapper/tree/main/sample_datasets%26outputs