作为人类重要的家畜和生物医学模型,猪的基因组研究一直是农业与生命科学领域的焦点。从肉质鲜美的地方品种到体型庞大的商业猪种,猪的表型差异背后藏着复杂的遗传密码。
近日,中国农业大学方美英教授与贾善刚老师团队在《Nature Genetics》发表的题为”Telomere-to-telomere genome assembly of a male pig provides insight into population structure and selection for body stature”研究。文章成功组装出首个猪T2T基因组,不仅填补了传统基因组的诸多空白,更揭示了猪种群演化规律与体型调控的分子机制,为猪育种改良与生物医药研究打开了全新视野。
对T2T基因组组装技术、跨物种分析、ChIP-seq 分析,基因功能验证等有需求的老师和同学快扫描二维码咨询,集思慧远全程为您提供优质服务!
译名:雄性猪T2T基因组为解析种群结构与体型选择机制提供新见解
期刊:nature genetics
IF:29.0
猪驯化已有近 10000 年历史,全球培育出 200 多个品种,但传统猪基因组组装存在大量缺口,着丝粒、端粒等重复区域未被完整解析,限制了遗传变异与性状关联的研究。五指山猪作为中国特有迷你猪品种,体型仅为商业猪的一半,是研究糖尿病、骨骼发育等疾病的理想模型,但其基因组的完整性与遗传特征尚未被充分挖掘。同时,猪的种群结构、不同品种体型差异的分子机制等关键问题,仍缺乏完整基因组数据的支撑,亟需高质量 T2T 基因组填补研究空白。
构建 五指山公猪T2T 基因组(T2T-pig1.0)。;比较基因组学分析解析着丝粒、Y 染色体等特殊区域的结构与演化;利用 407 个猪重测序数据更新种群遗传结构分析筛选与体型相关的候选基因,结合细胞实验验证 GALNT13 基因的功能,揭示猪体型调控的分子机制,为育种应用提供靶点。
猪 T2T 基因组组装
图1 T2 T-pig 1.0猪基因组组装
成功组装出 2.63Gb T2T-pig1.0 基因组,覆盖 18 条常染色体及 X、Y 染色体,0 gap且无未定位序列(Table 1)。基因组新增 194.42Mb 未解析区域(PURs),注释出 21713 个蛋白编码基因,其中 1189 个基因位于 PURs 中,这些基因在 hypothalamus 和垂体等组织中表达活跃(Fig. 1a,d)。
与传统 Sscrofa11.1 相比,T2T-pig1.0 的重复序列注释更完整,其中 DNA 转座子含量从 85.34Mb 提升至 145.93Mb(Table 1),还精准解析了 45S rDNA 区域,确认其在 chr8 和 chr10 上有 66 个拷贝(Fig. 1e,f)。
表1 猪基因组组装Sscrofa11.1和T2 T-pig 1.0的比较
猪着丝粒的全基因组结构
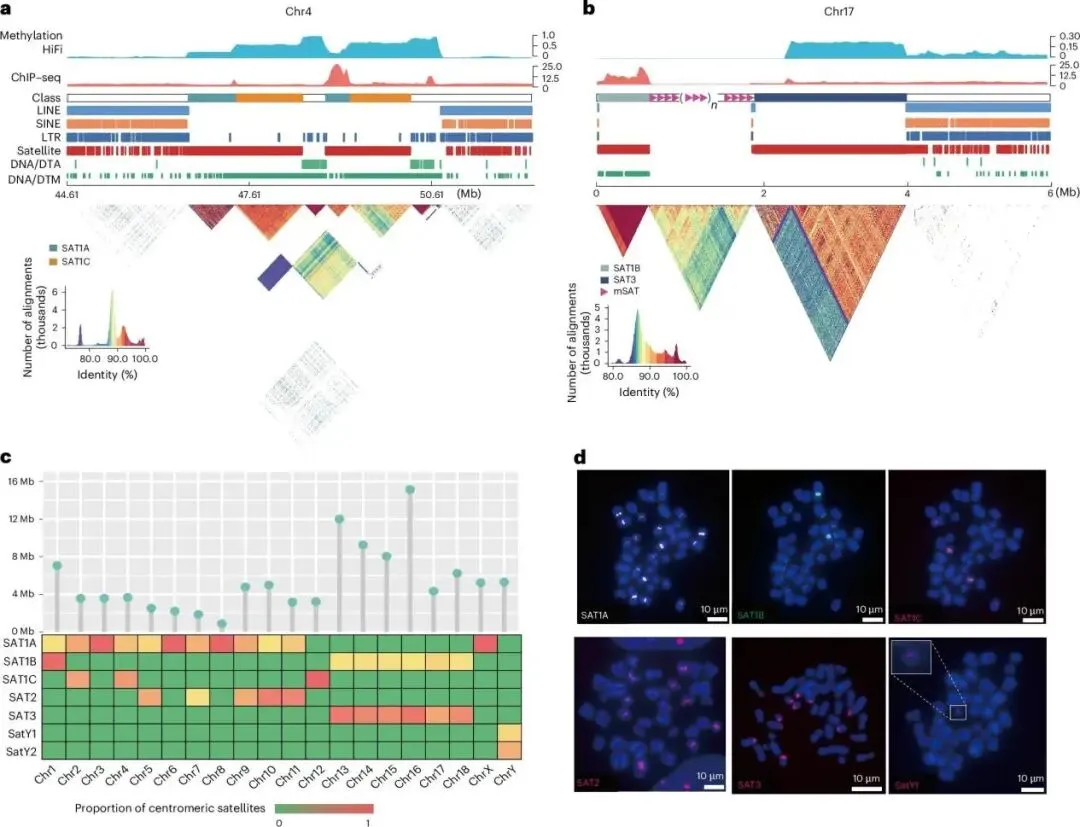
图2 T2 T-pig 1.0猪基因组组装中的着丝粒结构
通过 CENP-A ChIP-seq 与甲基化分析,研究团队鉴定出所有染色体的着丝粒区域,总长约 107.3Mb(Fig. 2a,b)。着丝粒主要由 SAT1、SAT2、SAT3 三类卫星重复序列组成,且端着丝粒染色体(chr13–chr18)具有 “端粒 - SAT1B-(mSAT)ₙ-SAT3-q 臂” 的独特结构,其中 mSAT(AGAAT)微卫星序列在着丝粒核心区域富集(Fig. 2b,c)。此外,着丝粒区域存在大量年轻 LTR 反转录转座子,远年轻于全基因组平均水平,提示 LTR 可能参与着丝粒演化。
Y 染色体分析及跨物种比较基因组分析
图3 Y 染色体特性
T2T-pig1.0 基因组首次实现 Y 染色体的无缺口组装,全长 43.25Mb,新增 29.64Mb 未知序列(Fig. 3)。注释出 111 个蛋白编码基因,其中 42 个为新鉴定基因,包括 14 个 HSFY 基因拷贝。跨物种比较发现,猪、人、山羊、绵羊的 Y 染色体雄性特异性区域(MSY)存在 11 个保守同源基因(如 SRY、TSPY),这些基因与精子发生和睾丸发育相关(Fig. 4b)。此外,猪 Y 染色体 q 臂富含 SatY3 卫星重复序列(20.98Mb),与人类 Y 染色体的异染色质区域特征相似(Fig. 3)。
群体结构分析
图4 变异识别和总体群体结构的改善
以 T2T-pig1.0 为参考对 407 个全球猪进行种群遗传分析,检测到 1784 万个 SNP,其中 339092 个位于 PURs 中(Fig. 5a)。种群结构分析将其分为亚洲家猪、欧洲家猪、北美家猪等 6 个类群,发现东北亚猪群中存在欧洲血统的基因渗透,更新了传统种群分类(Fig. 5c,d,e)。与 Sscrofa11.1 相比,T2T-pig1.0 显著提升了测序 reads 的比对率,减少了单端映射 reads 数量,使种群遗传分析更精准(Fig. 5b)。
与身高相关的选择特征
图5 GALNT 13与猪软骨细胞发育的关系
迷你猪(五指山猪、巴马香猪)与大型商业猪(杜洛克、大白猪)的选择性清除分析表明筛选出 280 个位于 PURs 的候选选择区域,涉及 657 个基因(Fig. 6a)。其中 GALNT13 基因表现出强烈的选择信号,该基因在猪的胸椎软骨、骨骺软骨等骨相关组织中高表达(Fig. 6a,b)。功能实验显示,GALNT13 过表达可抑制猪软骨细胞增殖,同时促进软骨细胞分化标志物(COL2A1、SOX9、RUNX2)的表达(Fig. 6d–i),提示其通过调控软骨细胞发育影响猪的体型大小。
本研究成功构建了首个猪 T2T-pig1.0基因组,填补了 194.42Mb 的基因组空白,准确性与完整性达到国际领先水平。文章解析了猪着丝粒的独特结构与演化规律,发现端着丝粒染色体的特异性序列排布,丰富了哺乳动物着丝粒演化的理论。完整解析了 Y 染色体的复杂结构,鉴定出 11 个跨物种保守的雄性特异性基因,为雄性生殖发育研究提供了重要资源。基于全球 407 个猪样本的重测序数据,更新了种群遗传结构,揭示了跨大陆基因渗透现象,为猪的驯化起源与扩散研究提供了新视角。此外,挖掘并验证了体型调控关键基因 GALNT13,阐明其通过调控软骨细胞增殖与分化影响猪体型的分子机制,为猪精准育种提供了核心靶点。研究不仅推动了猪基因组学研究的跨越式发展,也为其他家畜的 T2T 基因组组装与功能研究提供了可借鉴的范式,兼具重要的理论意义与应用价值。
南京集思慧远生物科技有限公司(Genepioneer Biotechnologies)坐落于美丽的“六朝古都”—南京,是江苏省内专业从事高通量测序服务的高科技企业。公司拥有一支高水平的科技人才队伍,其中博硕士研究生占90%以上,核心骨干人员从事高通量测序领域10年以上。
公司开发了一系列多组学/分子/理化检测的研究服务,如动植物基因组denovo测序、细胞器基因组测序、重测序、简化测序,转录组、蛋白组、代谢组检测分析,m6A-seq、DAP-seq、ATAC-seq、甲基化等表观组测序,以及荧光定量、植物遗传转化、EMSA、双荧光素酶、ChIP-qPCR等分子生物学实验,生物理化性质测定等。服务产品有近百种,涵盖动植物、微生物科学研究及人类健康等领域,获得了业内良好的口碑及高度认可,公司联系方式:025-83360120.
责编 | 冬冬
排版 | 山谷
审核 | 集思慧远产品部